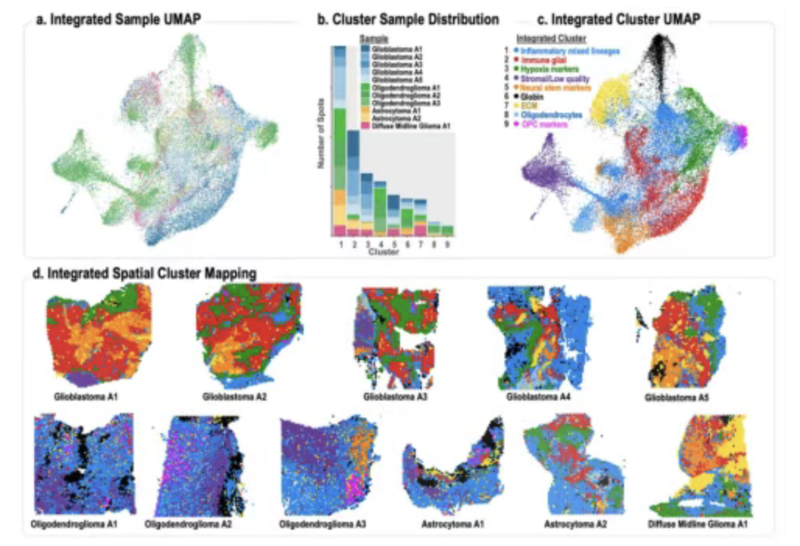
第一节:空间转录组在CNS文章应用
-
空间转录组CNS文章思路解析
-
空间转录组技术在科研领域的应用
-
空间转录组技术在不同科学等领域的研究内容及思路及常见图形解读
第二节 空间转录组R包Seurat分析及与单细胞联合分析实操
-
10x Visium官方分析软件Space Ranger输出结果解读,空间基因表达矩阵结构说明
-
Seurat基础分析流程:
-
降维方法:PCA、UMAP/t-SNE
-
聚类算法:分辨率参数设置与结果评估
-
可视化:空间点图与聚类分布展示
- Seurat高级功能应用:
-
基因表达空间可视化(FeaturePlot)
-
空间变量特征识别(Spatially Variable Features)
- 单细胞数据关联分
-
数据整合:锚点对齐与批次校正
-
空间细胞类型定义(细胞类型映射)
- 多样本整合分析
-
样本间差异处理
-
联合可视化与统计检验
第三节:python中squidpy和scanpy的分析流程
- Scanpy数据读取与预处理
-
数据导入:支持10X Visium等格式的空间转录组数据读取
-
质控流程:基因/细胞过滤、标准化、批次校正
- Scanpy核心分析流程
-
高变基因筛选(HVG)
-
降维方法:PCA、UMAP/t-SNE
-
聚类算法:Louvain/Leiden算法
-
可视化:二维/三维空间分布展示
- Scanpy差异基因分析
-
空间差异表达基因识别
-
统计检验与结果可视化
- Squidpy功能模块
-
图像特征计算:组织形态学量化
-
邻域富集分析(NPA)
-
空间差异基因分析
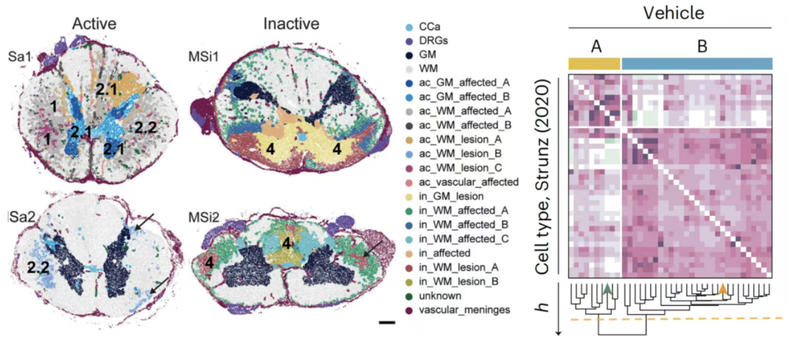
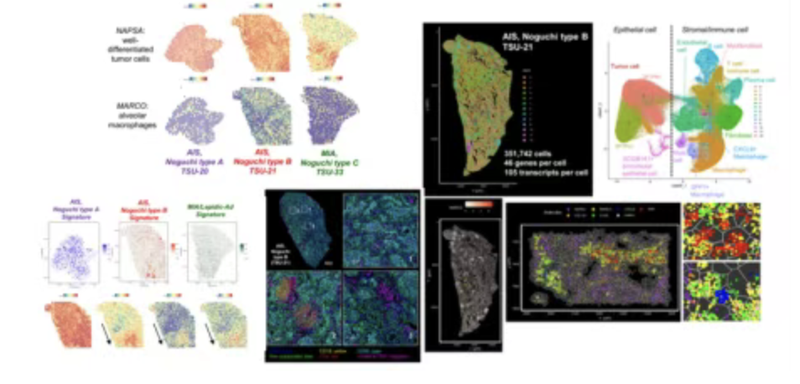
第四节:空间转录组基因表达分析、细胞反卷积及差异基因分析
- 空间转录组基因表达分析
-
R:Seurat包scTransform
-
Python:Tangram
- 细胞反卷积分析
-
R包:RCTD
-
Python:Cell2location
-
空间细胞类型解卷积实操
- 空间差异基因分析工具
-
跨平台SpatialDE(Python/R)
-
trendsceek与SPARK-R包
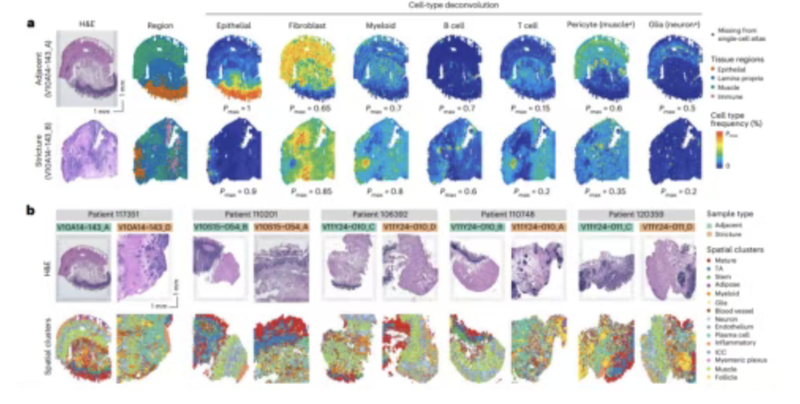
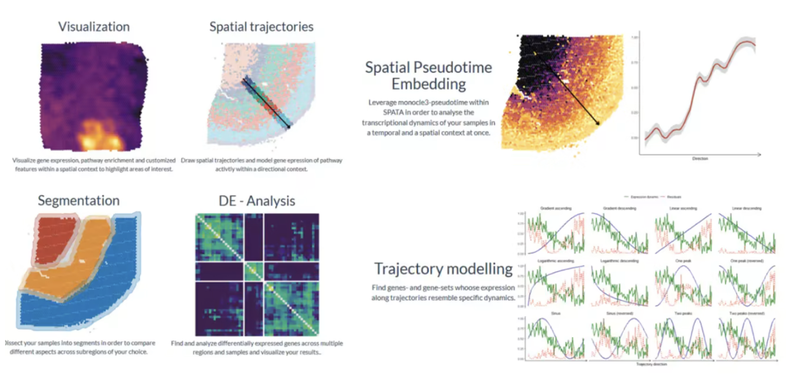
第五节:空间转录组的轨迹分析、细胞共定位分析
- 空间转录组的轨迹分析
-
R包:SPATA2实现
-
Python:stlearn实现
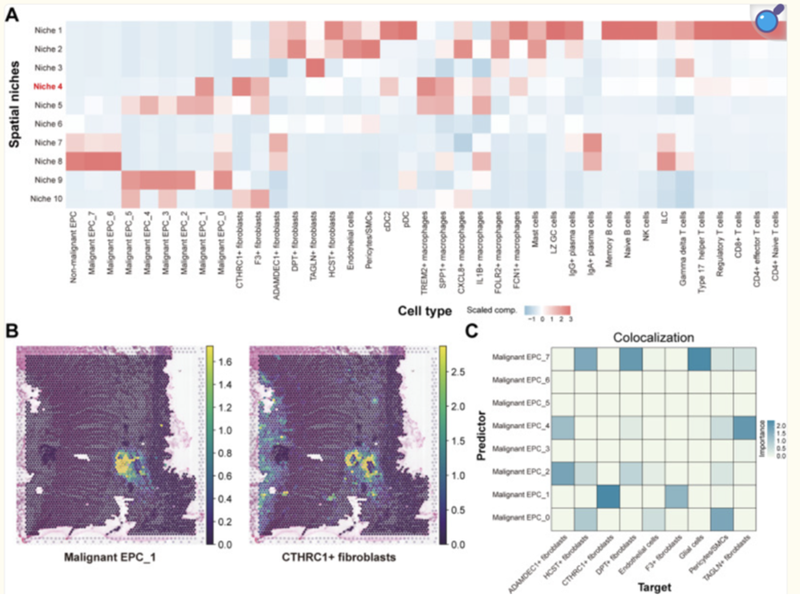
- 细胞共定位分析
-
R包:mistyR基础分析
-
扩展分析:细胞-通路-基因共定位
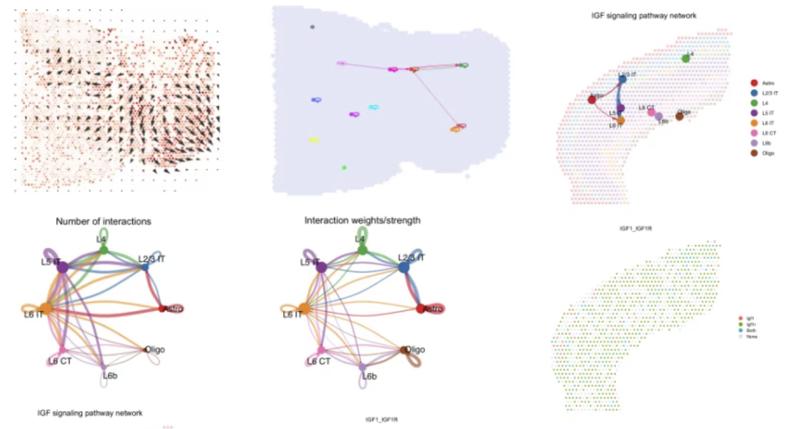
**第六节:空间转录组细胞通讯分析 **
-
R包CellChat:细胞通讯分析及可视化
-
R包NicheNet:分析配体对下游基因调控
-
Python库CellPhoneDB、COMMOT、stlearn细胞通讯分析及可视化
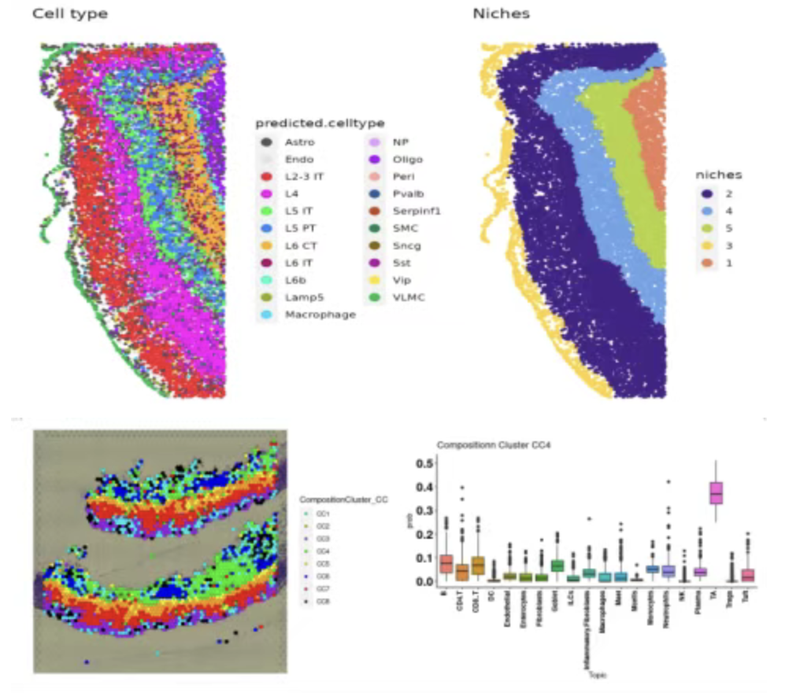
第七节:空间转录组细胞生态位及分子生态位分析
- 基础矩阵类型
- 基因表达矩阵、细胞类型矩阵、细胞生态位矩阵、分子生态位矩阵
- 生态位差异分析和聚类方法
- R包nicheDE:生态位差异表达
- Python及R包Banksy:生态位聚类
- 细胞niche分析
- R包Seurat、R包ISCHIA